AFLP Molecular Markers-based Genetic Diversity Analysis on 90 Avocado Germplasms
-
摘要:目的 本研究对采自中国云南德宏、保山、西双版纳、普洱、红河和缅甸克钦邦、掸邦地区共90份鳄梨种资资源进行遗传多样性分析,为其新品种选育和种质创新提供参考依据。方法 采用CTAB法提取鳄梨叶片基因组DNA,利用扩增片段长度多态性分子标记技术,对90份种质资源的基因组DNA进行酶切、连接、预扩增、选择性扩增,电泳分离,银染显色。电泳结果得到“0,1”矩阵,使用POPGENE 32软件计算每对引物的多态性条带、多态性比率、有效等位基因数、遗传多样性指数等指标,同时使用NTSYSpc-2.11F计算种质间遗传相似系数,根据相似性系数进行UPGMA聚类分析和PCA主效应分析,对鳄梨种质资源进行分类。结果 从24对AFLP引物组合中,筛选出8对扩增条带清晰、多态性高的引物组合,8对引物共扩增出1 165个条带,其中多态性条带有1 163个,多态位点百分率为99.83%;有效等位基因数(Ne)平均1.294 4个;Nei’s基因多样性指数(H)平均0.209 5;Shannon信息指数(I)平均0.353 0。根据遗传相似系数进行聚类分析,在遗传相似系数0.752处可划分为4个类群,第I类群有1份保山种质70号;第II类群有24份种质;第III类群有1份西双版纳种质59号;第IV类群有64份种质。在遗传相似系数0.763处可将第IV类群划分为3个亚群(A、B和C)。用PCA法对90份鳄梨种质AFLP标记结果进行主效应分析,显示了不同种质的分类位置,主效应分析结果与分子聚类结果基本一致,呈一定的地域性分布规律。结论 90份种质资源的遗传多样性较为丰富,59号和70号相对特殊,在种质创新中应给予重点关注。Abstract:Objective Genetic relationship of 90 avocado (Persea americana Mill.) germplasms collected from Dehong, Baoshan, Xishuangbanna, Puer, and Honghe in Yunnan, China and Shan and Kachin States of Burma was analyzed based on AFLP molecular markers for breeding reference and resource information.Method Genomic DNAs were extracted from the leaves of the avocado plants following the CTAB method. They were amplified using the sequence-related amplified polymorphism molecular markers to determine their genetic diversity and similarity. Separation of the amplified fragments was performed on 5% denaturing polyacrylamide gels stained with AgNO3 to obtain the “0,1” matrix. The number of polymorphic loci, percentage of polymorphic loci, effective number of alleles, and indices of genetic diversity were estimated by POPGENE version 32. The genetic similarity estimated by NTSYSpc-2.11F was used for UPGMA (unweighted pair group method analysis) and PCA (principal component analysis) to classify the avocado germplasms.Result Eight primers with strong polymorphism and high repeatability were screened from 24 AFLP primers generating a total of 1 165 bands. Of the bands, 1 163 (99.83%) showed polymorphism. On average, the number of effective alleles was 1.294 4; Nei's gene diversity (H), 0.209 5; and Shannon's information index (I), 0.353 0. At the genetic similarity index (GS) of 0.752, the germplasms were classified into 4 groups. A single avocado germplasm, No. 70, collected from Baoshan was placed in Group I. Group II had 22 germplasms; Group III, one germplasm, No. 59, from Xishuangbanna; and Group IV, the 64 remainders. The germplasms in Group IV were further divided into Subgroups A, B and C at GS of 0.763. A similar grouping result was obtained from the cluster analysis on the PCR data applied AFLP markers confirming these germplasms shared a high similarity within a same region.Conclusion The 90 collected avocado germplasms were found to be relatively high in genetic diversity. Among them, No. 59 and 70 stood out as two most unique varieties.
-
Keywords:
- Avocado (Persea americana Mill) /
- AFLP /
- genetic diversity
-
0. 引言
【研究意义】鳄梨Persea americana Mill.,又称牛油果、油梨、酪梨、幸福果等,为樟科Lurcee鳄梨属Persea常绿落叶乔木[1]。鳄梨脂肪含量高,含有大量的酶,有健胃清肠的作用,并具有降低胆固醇和血脂、保护心血管和肝脏系统等重要生理功能,味如乳酪,有“森林黄油”之美称,是一种集营养与保健为一身的水果[2]。随着人们对鳄梨认识的提高,鳄梨需求量逐年大幅增长。2016年中国鳄梨进口量已达到42 510 t,是2012年进口量的14.8倍, 进口额达12 176.7万美元[3]。
鳄梨自然分布是以中美洲为中心,分布范围从热带的哥伦比亚至墨西哥南部的高山亚热带地区。根据原产地生态条件的不同,鳄梨主要分为3个种系,即危地马拉系、墨西哥系和西印度系。由于鳄梨的3个种系之间不存在杂交障碍,目前大多数商业鳄梨品种是这3个种系间的杂交种[4]。中国引进的资源主要是危地马拉系及其杂交种,云南、海南、广西、广东、福建、四川、浙江、贵州等省(区)都有种植,且种植面积和产量呈快速上升趋势。缅甸及云南等地现存丰富的鳄梨资源,经历了各种不良气候和病虫害侵袭,自然适者生存,迄今拥有良好的适应性、抗逆性以及其他多种优异性状。因此,系统开展缅甸及云南地区野生、半野生鳄梨种质资源的调查、收集、保存及利用,选育新品种,对促进产业健康发展和开发利用该地区独特鳄梨资源具有重要意义。
【前人研究进展】AFLP(扩增片段长度多态性)是限制性酶切与PCR扩增结合的一种分子标记技术,由荷兰科学家Zabeau[5]发明,是对DNA酶切片段存在的差异进行PCR扩增,进而产生片段多态性[6]。AFLP具有可靠性好,重复性强,可信度高等优点,广泛应用于建立鳄梨遗传图谱[7]、鳄梨根腐病[8]、鳄梨遗传多样性分析[9]等领域研究。【本研究切入点】尽管鳄梨产业发展迅速,但目前鳄梨产区栽培品种比较单一,中国90%以上种植美国选育的Hass(哈斯)品种,十分不利于产业的健康发展。【拟解决的关键问题】本研究搜集缅甸及云南等地鳄梨资源,调查滇缅鳄梨种质90份,采用AFLP标记对其进行遗传多样性分析,旨在明确鳄梨种质间的亲缘关系,为指导鳄梨新品种选育和种质创新研究提供借鉴。
1. 材料与方法
1.1 试验材料
试验材料共90份(表1),主要采集地点在滇缅边境地区,包括缅甸克钦邦的八莫、掸邦的南坎以及云南省西双版纳、德宏州、红河州、普洱及保山。
表 1 供试鳄梨种质资源信息Table 1. Avocado germplasms studied序号
Number种质编号
Germplasm code序号
Number种质编号
Germplasm code序号
Number种质编号
Germplasm code来源地:缅甸克钦邦八莫市
Origin: Bhamo, Kachin state,
Myanmar来源地:云南省普洱市孟连县
Origin: Menglian County, Pu'er City,
Yunnan Province62 EL0062 63 EL0063 64 EL0064 1 EL0001 32 EL0032 65 EL0065 2 EL0002 33 EL0033 来源地:云南省德保山市潞江坝
Origin: Lujiangba, Baoshan City,
Yunnan Province3 EL0003 34 EL0034 4 EL0004 35 EL0035 5 EL0005 36 EL0036 66 EL0066 6 EL0006 37 EL0037 67 EL0067 7 EL0007 38 EL0038 68 EL0068 8 EL0008 39 EL0039 69 EL0069 9 EL0009 40 EL0040 70 EL0070 10 EL0010 41 EL0041 来源地:云南省德宏州盈江县
Origin: Yingjiang County, Dehong Prefecture, Yunnan Province11 EL0011 42 EL0042 12 EL0012 43 EL0043 13 EL0013 71 EL0071 来源地:缅甸掸邦南坎
Origin: Namhkam, Shan State,
Myanmar来源地:云南省热带作物科学研究所
Origin: Yunnan Institute of
Tropical Crops72 EL0072 73 EL0073 74 EL0074 14 EL0014 44 EL0044 75 EL0075 15 EL0015 45 EL0045 76 EL0076 16 EL0016 46 EL0046 来源地:云南省德宏州瑞丽市
Origin: Ruili City, Dehong Prefecture,
Yunnan Province17 EL0017 47 EL0047 18 EL0018 48 EL0048 19 EL0019 49 EL0049 77 EL0077 20 EL0020 50 EL0050 78 EL0078 21 EL0021 51 EL0051 79 EL0079 22 EL0022 52 EL0052 80 EL0080 23 EL0023 53 EL0053 81 EL0081 来源地:云南省红河州元阳县
Origin: Yuanyang County, Honghe Prefecture, Yunnan Province54 EL0054 82 EL0082 55 EL0055 83 EL0083 56 EL0056 84 EL0084 24 EL0024 57 EL0057 85 EL0085 25 EL0025 来源地:云南省西双版纳州景洪县
Origin: Jinghong County, Xishuangbanna
Prefecture, Yunnan Province86 EL0086 26 EL0026 来源地:云南省德宏州芒市
Origin: Mangshi City, Dehong Prefecture,
Yunnan Province27 EL0027 28 EL0028 58 EL0058 87 EL0087 29 EL0029 59 EL0059 88 EL0088 30 EL0030 60 EL0060 89 EL0089 31 EL0031 61 EL0061 90 EL0090 1.2 基因组总DNA的提取
每种材料采取6个单株叶片混合,装入含有硅胶的自封袋,干燥后放入−20℃冰箱中,采用CTAB法[10]提取样品基因组DNA,0.8%琼脂糖凝胶电泳检测DNA质量及浓度,将样品稀释到20 ng·uL−1,−20℃保存备用。
1.3 主要试剂及引物
Taq 酶 (2 U·uL−1)、10×PCR buffer、dNTP (10 mmol· L−1)、引物(10 mmol·L−1)、内切酶(10 U·uL−1) (NEB公司)、T4DNA连接酶(5 U·uL−1) 购自NEB公司。Marker为DL2000、100 bp DNA Ladder,分子量内标为ROX500(ABI公司)。8对引物(3-2、3-3、3-6、4-2、7-1、7-3、9-2、10-2) 由北京鼎国昌盛生物技术有限责任公司合成,正向引物均为FAM标记,试验所用接头和引物信息见表2。
表 2 引物系列Table 2. Primer sequence接头与引物 Connector and primer 系列(5′-3′) Sequence Eco RI 接头1(Eco RI Connector 1) CTCGTAGACTGCGTACC Eco RI 接头2 (Eco RI Connector 2) AATTGGTACGCAGTCTAC Mse I 接头1 (Mse IConnector 1) GACGATGAGTCCTGAG Mse I 接头2 (Mse I Connector 2) TACTCAGGACTCAT 3-2引物 (3-2 primer) E-AAC/M-CAC 3-3引物 (3-3 primer) AAC/M-CAG 3-6引物 (3-6 primer) E-AAC/M-CTC 4-2引物 (4-2 primer) E-AAG/M-CAC 7-1引物 (7-1 primer) E-ACC/M-CAA 7-3引物 (7-3 primer) E-ACC/M-CAG 9-2引物 (9-2 primer) E-AGC/M-CAC 10-2引物 (10-2 primer) E-AGG/M-CAC 1.4 AFLP扩增及检测
首先选用6个鳄梨品种(1、15、25、40、60、70号)进行引物筛选,从24对引物中筛选出8对引物,然后进行90份材料的整体试验。
酶切-连接:对所选样品采用 EcoRⅠ/MseⅠ双酶切,酶切与连接反应同步进行。
(1)酶切与连接体系为: 10×Reacton buffer 2.5 uL, Adapter 1. 0 uL,Eco RI /Mse I 2 uL,10 mmol·L−1ATP 2.5 uL,T4 Ligase 1 uL,模板DNA 4 μL(50 ng·uL−1),补ddH2O至20 uL。酶切-连接反应条件为37℃保温5 h,8℃保温4 h,4℃过夜,1.5%琼脂糖凝胶电泳检测。
(2)预扩增反应体系:模板DNA 2 uL,Pre-ampmix(预扩引物)1 uL,dNTPs 1 uL,10×PCR buffer 2.5 uL,Tap酶0.5 uL,加ddH2O至25 uL。PCR扩增程序为94℃预变性2 min;94℃变性30 s;56℃复性30 s;72℃延伸80 s,30个循环。
(3)选择性扩增反应体系:Eco RI引物1 uL,Mse I引物1 uL,10×PCR buffer 2.5 uL,dNTP 0.5 uL,Taq酶0.5 uL,模板DNA 2 uL,加ddH2O至25 uL。PCR扩增程序为:95℃预变性5 min,94℃变性30 s,65℃复性30 s,72℃延伸80 s,12个循环,94℃变性30 s,55℃复性30 s,72℃延伸80 s,23个循环。
(4)将甲酰胺与分子量内标按100∶1的体积比混匀后,取9 uL加入上样板中,再加入1 uL稀释10倍的PCR产物,然后使用ABI377测序仪进行电泳检测。
1.5 数据分析
利用GENESCAN3.1软件将90份样品、8对引物组合扩增得到的原始数据进行分析,软件每2个碱基读取1次,Marker片段范围为70~500 bp,软件BinThere设置范围为69.5~501.5,一共读取216条条带,在原始数据基础上,有记作“1”,无则记为“0”,构成0,1数据矩阵。根据Nei等的方法[11-12],利用POPGENE 32软件分析有效等位基因数(Ne)、Nei’s基因多样性指数(H)和Shannon 信息指数(I)等。同时使用NTSYSpc-2.11F软件计算遗传相似系数(GS)[13],根据相似性系数进行UPGMA聚类分析[14]和PCA主效应分析。
2. 结果与分析
2.1 AFLP扩增条带的多态性及遗传多样性分析
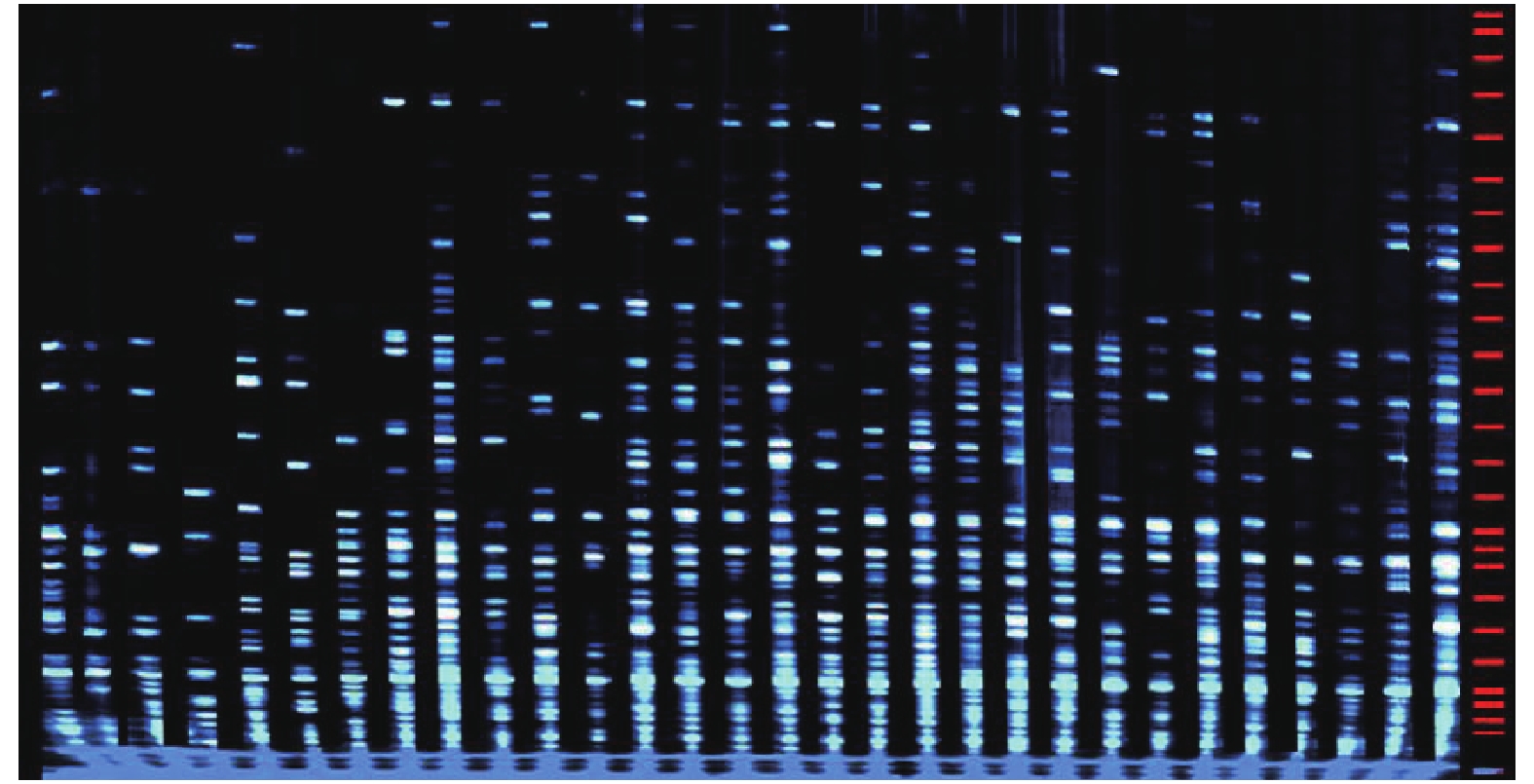
选用8对AFLP引物组合对90份鳄梨种质资源进行扩增,结果见表3和图1。8对引物组合共扩增出1 165条带,其中多态性条带为1 163条,占总条带数的99.83%,表明利用这8对引物可以进行基因多态性检测,且90份鳄梨种质资源多态性较高;有效等位基因数(Ne)范围1.257 9~1.329 1个,平均1.294 4个;Nei’s基因多样性指数(H)范围0.188 5~0.225 8,平均0.209 5;Shannon 信息指数(I)范围0.325 0~0.374 3,平均0.353 0,具有较丰富的遗传多样性。
表 3 8对引物组合扩增的AFLP条带Table 3. Amplification bands with 8 pairs of AFLP primers引物组合
Primer pair总条带数
Total bands多态性条带数
Polymorphic bands多态性比率
Polymorphic rate/%有效等位基因数
NeNei’s基因多样性
HShannon’s多样性
IE-AAC/M-CAC 144 144 100 1.306 1 0.215 3 0.359 9 F-AAC/M-CAG 145 144 99.31 1.257 9 0.188 5 0.325 0 E-AAC/M-CTC 136 135 99.26 1.329 1 0.225 6 0.372 2 E-AAG/M-CAC 147 147 100 1.294 8 0.209 9 0.353 3 E-ACC/M-CAA 147 147 100 1.322 5 0.225 8 0.374 3 E-ACC/M-CAG 150 150 100 1.268 6 0.197 2 0.337 9 E-AGC/M-CAC 141 141 100 1.313 7 0.218 8 0.365 2 E-AGG/M-CAC 155 155 100 1.262 1 0.194 9 0.335 8 平均 Mean 145.63 145.38 99.83 1.294 4 0.209 5 0.353 0 总和 Total 1 165 1 163 2.2 聚类分析
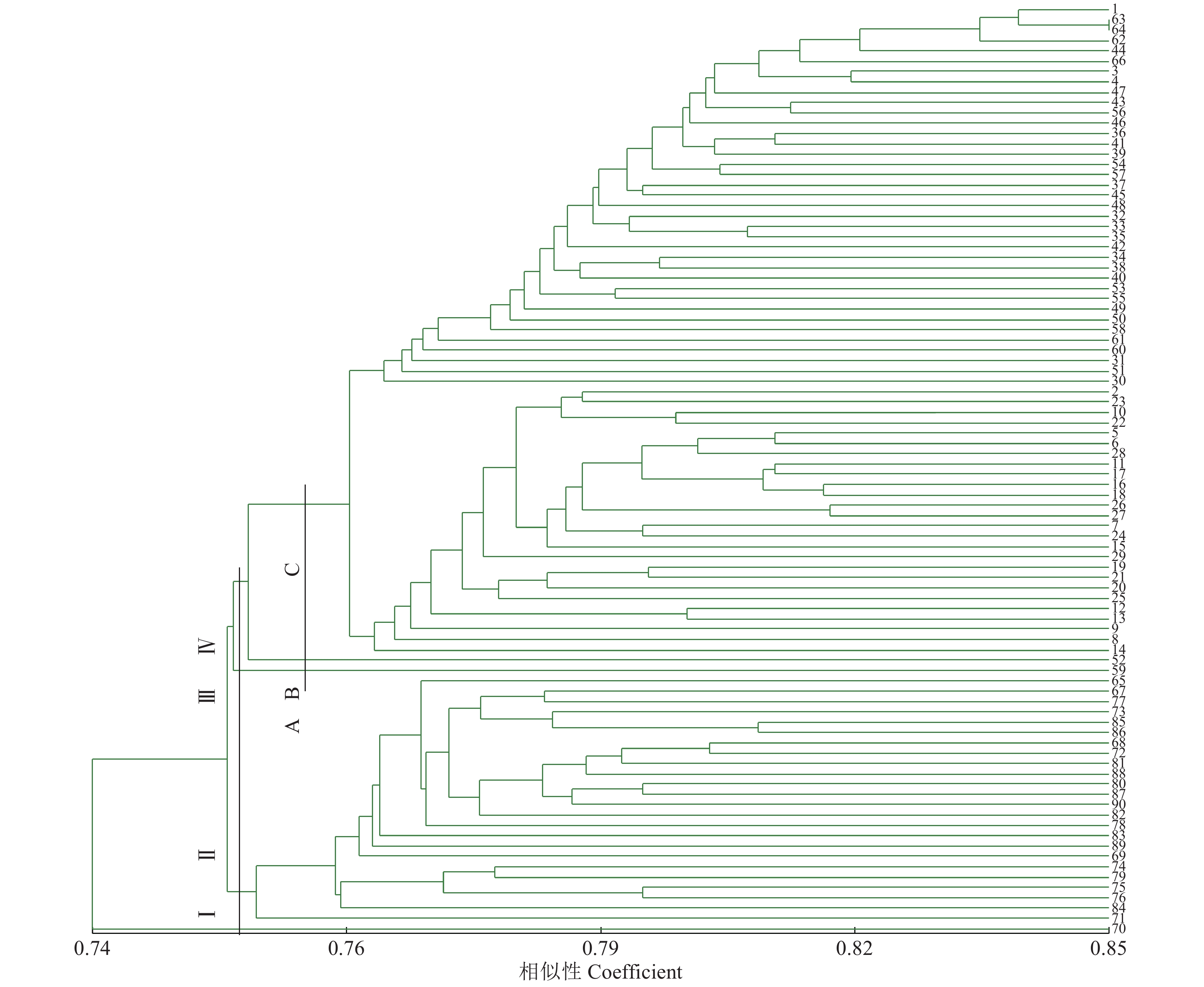
根据遗传相似系数,用UPGMA法对90份鳄梨种质进行聚类分析(图2)。从图2可知,在相似性系数0.752处切割时,可划分为四大类群,第I类群有1份种质,采集于保山潞江坝70号;第II类群共有24份种质,其中包括20份采集于德宏的全部资源71~90号,此外还包括4份采集于保山的65、67、68、69号;第III类群有1份种质,采集于西双版纳 的景洪59号;第IV类群有64份种质。在相似性系数0.763处切割,可将IV类群划分为3个亚群(A、B和C)。A亚群包含1份采集于西双版纳云南省热带作物科学研究所的52号;B亚群包含27份种质,其中采集于缅甸的20份,红河元阳7份24~30号;C亚群包括36份种质,其中包括1份采集于红河元阳的31号,3份采集于缅甸八莫的1、3、4号,1份采集于保山潞江坝的77号,12份采集于普洱孟连、19份采集于西双版纳(12份采集于云南省热带作物科学研究所、7份采集于景洪)。
2.3 主效应分析
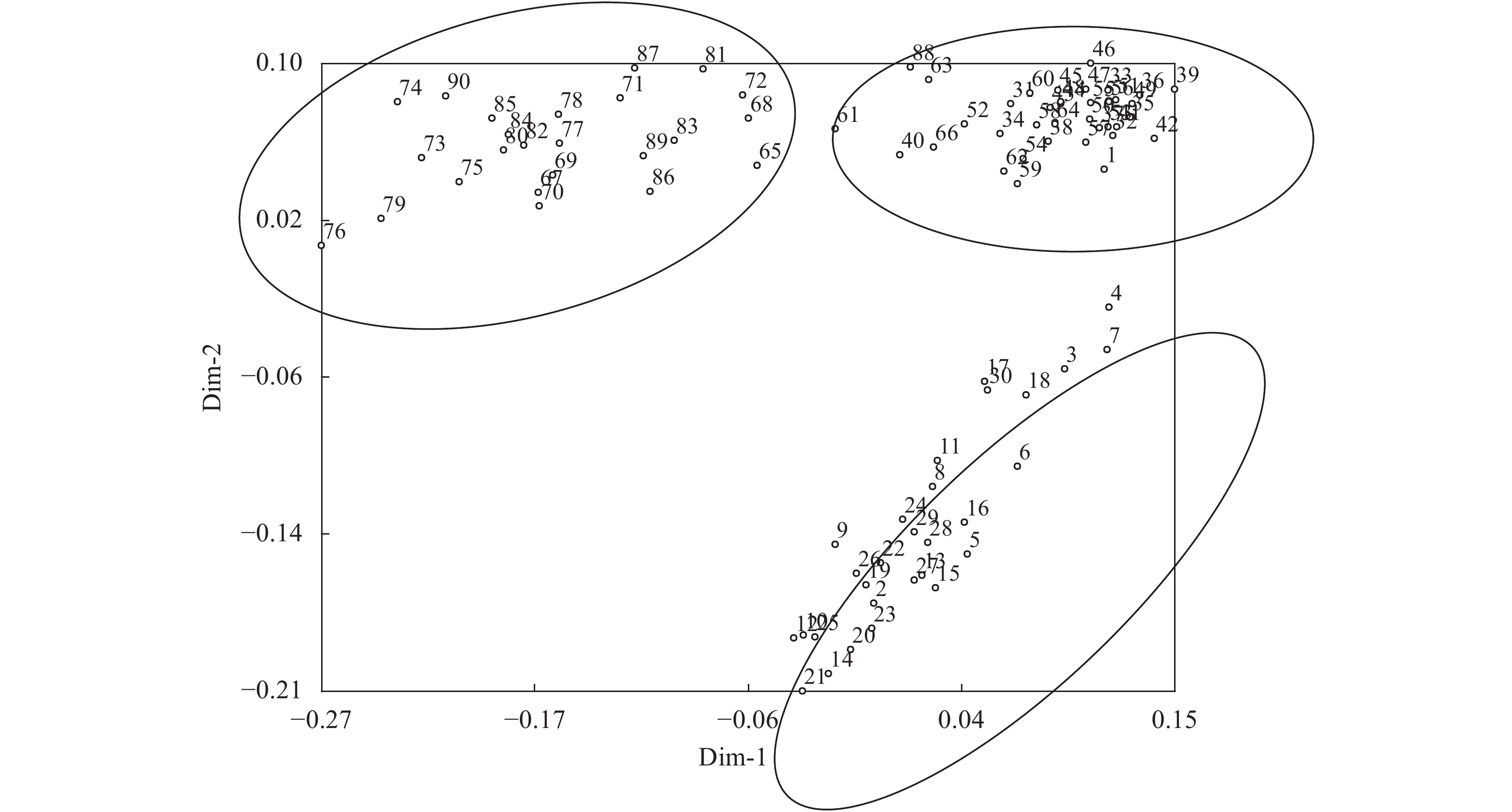
主效应分析显示了不同鳄梨种质的分类位置,结果如图3所示,将位置靠近的材料归为一类,可分为3个主要类群。其中2~30号共29份材料聚为一个类群,主要采集地为缅甸和红河;31~64号以及1号、66号和88号共37份材料聚在一个类群,主要采集地为普洱孟连和西双版纳;67~87号以及65、89、90号共24份材料聚在一个类群,主要采集地为保山和德宏。主效应分析结果与聚类分析结果基本一致,缅甸和红河元阳采集的资源聚为一类,普洱孟连和西双版纳采集的资源聚为一类,保山和德宏采集的资源聚为一类。集中在一个区域的种质亲缘关系较为紧密,1号虽然采集地为缅甸,但2种聚类结果都将其划分到普洱孟连和西双版纳一类,所以1号种质与孟连及西双版纳资种质的亲缘关系更为紧密。
3. 讨论与结论
3.1 AFLP分子标记是研究鳄梨遗传多样性的有效工具
具有丰富多样性的种质资源是果树育种的前提和重要基础,多种分子标记已应用于鳄梨的物种分类、亲缘关系鉴定、病毒检测、遗传特性评价及指纹图谱构建等领域[15-23]。利用AFLP分子标记是检测种质亲缘关系和种质资源遗传多样性的有效手段。Dohuan等[9]利用AFLP标记在83个鳄梨砧木品种中,共鉴定出61个多态性标记,并通过UPMGA进行遗传多样性分析和各基因型材料的聚类分析,将这些鳄梨砧木资源对根腐病的抗性分为易感、中度耐受、耐受和高度耐受等4类。Rodriguez等[24]利用AFLP、ISTR,SSR、同工酶标记以及形态标记共5种标记对17份鳄梨种质进行多态性水平分析,结果证明单独用AFLP或ISTR就可以将所有的材料鉴定出来。本试验利用8对AFLP引物组合共扩增出1 165条带,其中多态性条带为1 163条,占总条带数的99.83%,表明利用这8对引物可以进行基因多态性检测,Shannon多态性信息指数平均0.353 0,说明这些资源具有较丰富的遗传多样性。
3.2 聚类分析和主成分分析在鳄梨种质资源遗传多样性中的应用
本试验通过AFLP聚类分析得出,在相似系数为0.752时,将90份资源分为四大类,第I大类和第III大类各有1份种质,分别来源于保山潞江坝和西双版纳景洪,说明这2份资源的亲缘关系较其他材料较远,其中来自于保山潞江坝的70号果实具有较浓的苦味,相比其他资源品质特色,其苦味成分及含量有待下一步研究。第II类,共有24份种质,占总资源的26.67%,主要来源于德宏和保山,说明德宏和保山的资源亲缘关系较近。第IV大类群共有64份种质,占总资源的71.11%,在相似系数为0.763时,又可将其划分为3个亚群,其中A亚群只有1份材料来自于西双版纳的52号;B亚群共有27份材料,来源于缅甸和红河,说明采集于缅甸和红河的种质资源亲缘关系相对较亲密;C亚群共有36份材料,主要来源于普洱孟连和西双版纳,说明这2个地方的资源亲缘关系较近。从地理位置来说,德宏和保山相邻,普洱和西双版纳相邻,但红河和缅甸相隔较远,相反德宏、普洱和西双版纳都与缅甸接壤,但可能原因是红河引进的资源来源于缅甸。主成分分析结果和聚类分析结果相似,呈现明显的地域性分布规律,相同和相近地理来源的材料能聚在一起。
本研究系统开展了缅甸及云南地区野生、半野生鳄梨种质资源的调查、收集与保存。通过AFLP分子标记技术,综合分析了90份鳄梨资源的遗传多样性水平,为选育新品种促进产业健康可持续发展和开发利用该地区独特鳄梨资源奠定良好基础。
-
表 1 供试鳄梨种质资源信息
Table 1 Avocado germplasms studied
序号
Number种质编号
Germplasm code序号
Number种质编号
Germplasm code序号
Number种质编号
Germplasm code来源地:缅甸克钦邦八莫市
Origin: Bhamo, Kachin state,
Myanmar来源地:云南省普洱市孟连县
Origin: Menglian County, Pu'er City,
Yunnan Province62 EL0062 63 EL0063 64 EL0064 1 EL0001 32 EL0032 65 EL0065 2 EL0002 33 EL0033 来源地:云南省德保山市潞江坝
Origin: Lujiangba, Baoshan City,
Yunnan Province3 EL0003 34 EL0034 4 EL0004 35 EL0035 5 EL0005 36 EL0036 66 EL0066 6 EL0006 37 EL0037 67 EL0067 7 EL0007 38 EL0038 68 EL0068 8 EL0008 39 EL0039 69 EL0069 9 EL0009 40 EL0040 70 EL0070 10 EL0010 41 EL0041 来源地:云南省德宏州盈江县
Origin: Yingjiang County, Dehong Prefecture, Yunnan Province11 EL0011 42 EL0042 12 EL0012 43 EL0043 13 EL0013 71 EL0071 来源地:缅甸掸邦南坎
Origin: Namhkam, Shan State,
Myanmar来源地:云南省热带作物科学研究所
Origin: Yunnan Institute of
Tropical Crops72 EL0072 73 EL0073 74 EL0074 14 EL0014 44 EL0044 75 EL0075 15 EL0015 45 EL0045 76 EL0076 16 EL0016 46 EL0046 来源地:云南省德宏州瑞丽市
Origin: Ruili City, Dehong Prefecture,
Yunnan Province17 EL0017 47 EL0047 18 EL0018 48 EL0048 19 EL0019 49 EL0049 77 EL0077 20 EL0020 50 EL0050 78 EL0078 21 EL0021 51 EL0051 79 EL0079 22 EL0022 52 EL0052 80 EL0080 23 EL0023 53 EL0053 81 EL0081 来源地:云南省红河州元阳县
Origin: Yuanyang County, Honghe Prefecture, Yunnan Province54 EL0054 82 EL0082 55 EL0055 83 EL0083 56 EL0056 84 EL0084 24 EL0024 57 EL0057 85 EL0085 25 EL0025 来源地:云南省西双版纳州景洪县
Origin: Jinghong County, Xishuangbanna
Prefecture, Yunnan Province86 EL0086 26 EL0026 来源地:云南省德宏州芒市
Origin: Mangshi City, Dehong Prefecture,
Yunnan Province27 EL0027 28 EL0028 58 EL0058 87 EL0087 29 EL0029 59 EL0059 88 EL0088 30 EL0030 60 EL0060 89 EL0089 31 EL0031 61 EL0061 90 EL0090 表 2 引物系列
Table 2 Primer sequence
接头与引物 Connector and primer 系列(5′-3′) Sequence Eco RI 接头1(Eco RI Connector 1) CTCGTAGACTGCGTACC Eco RI 接头2 (Eco RI Connector 2) AATTGGTACGCAGTCTAC Mse I 接头1 (Mse IConnector 1) GACGATGAGTCCTGAG Mse I 接头2 (Mse I Connector 2) TACTCAGGACTCAT 3-2引物 (3-2 primer) E-AAC/M-CAC 3-3引物 (3-3 primer) AAC/M-CAG 3-6引物 (3-6 primer) E-AAC/M-CTC 4-2引物 (4-2 primer) E-AAG/M-CAC 7-1引物 (7-1 primer) E-ACC/M-CAA 7-3引物 (7-3 primer) E-ACC/M-CAG 9-2引物 (9-2 primer) E-AGC/M-CAC 10-2引物 (10-2 primer) E-AGG/M-CAC 表 3 8对引物组合扩增的AFLP条带
Table 3 Amplification bands with 8 pairs of AFLP primers
引物组合
Primer pair总条带数
Total bands多态性条带数
Polymorphic bands多态性比率
Polymorphic rate/%有效等位基因数
NeNei’s基因多样性
HShannon’s多样性
IE-AAC/M-CAC 144 144 100 1.306 1 0.215 3 0.359 9 F-AAC/M-CAG 145 144 99.31 1.257 9 0.188 5 0.325 0 E-AAC/M-CTC 136 135 99.26 1.329 1 0.225 6 0.372 2 E-AAG/M-CAC 147 147 100 1.294 8 0.209 9 0.353 3 E-ACC/M-CAA 147 147 100 1.322 5 0.225 8 0.374 3 E-ACC/M-CAG 150 150 100 1.268 6 0.197 2 0.337 9 E-AGC/M-CAC 141 141 100 1.313 7 0.218 8 0.365 2 E-AGG/M-CAC 155 155 100 1.262 1 0.194 9 0.335 8 平均 Mean 145.63 145.38 99.83 1.294 4 0.209 5 0.353 0 总和 Total 1 165 1 163 -
[1] WHILEY A W, SCHAFFER B, WOLSTENHOLME B N. The avocado: botany, production and uses [J]. Postharvest Biology & Technology, 2004(31): 213−214.
[2] 郑淑娟, 白净. 世界油梨产销发展概况及前景 [J]. 世界热带农业信息, 2011(11):6−9. DOI: 10.3969/j.issn.1009-1726.2011.11.016 ZHENG S J, BAI J. Development of avocado production and marketing and prospects in the world [J]. World Tropical Agriculture Information, 2011(11): 6−9.(in Chinese) DOI: 10.3969/j.issn.1009-1726.2011.11.016
[3] FAO[DB/OL]. http://www.fao.org/faostat/en/#data.
[4] WHILEY A W, SCHAFFER B, WOLSTENHOLME B N. The avocado: botany, production and uses[M]. Wallingford: CABI, 2002.
[5] ZABEAU M, VOS P. Selective restriction fragment amplification: a general method for DNA fingerprinting[M]. European Patent Application 92402629. 7(Publication No. 0534858A1). Paris: European Office, 1993.
[6] VOS P, HOGERS R, BLEEKER M, et al. AFLP: a new technique for DNA fingerprinting [J]. Nucleic Acids Research, 1995, 23(21): 4407−4414. DOI: 10.1093/nar/23.21.4407
[7] FARROW B J, FOURIE G, VAN DEN BERG N. DNA profiling of Persea americana using AFLP markers [J]. South African Journal of Botany, 2010, 76(2): 410.
[8] ZENTMYER G A. Phytophthora cinnamomi and the diseases it causes[M]. Monogr 10, Am Phytopathol Soc, St Paul, Minnesota. 1980: 96.
[9] DOUHAN G W, FULLER E, MCKEE B, et al. Genetic diversity analysis of avocado (Persea americana Miller) rootstocks selected under greenhouse conditions for tolerance to Phytophthora root rot caused by Phytophthora cinnamomi [J]. Euphytica, 2011, 182(2): 209−217. DOI: 10.1007/s10681-011-0433-y
[10] AHMAD F, MEGIA R, POERBA Y S. Genetic diversity of Musa balbisiana Colla in Indonesia based on AFLP marker [J]. HAYATI Journal of Biosciences, 2014, 21(1): 39−47. DOI: 10.4308/hjb.21.1.39
[11] NEI M, LI W H. Mathematical model for studying genetic variation in terms of restriction endonucleases [J]. Proceedings of the National Academy of Sciences of the United States of America, 1979, 76(10): 5269−5273. DOI: 10.1073/pnas.76.10.5269
[12] SHANNON C E, WEAVER W. The mathematical theory of communication[M]. Urbana: University of Illinois Press, 1949: 170 − 180.
[13] ROHLF F J. NTSYS-pc: numerical taxonomy and multivariate analysis system, version 2.1[M]. New York: Exeter Software, 2000.
[14] NEI M, KUMAR S. Molecular evolution and phylogenetics[M]. Molecular evolution and phylogenetics, 2000: 87 − 88.
[15] ASHWORTH V, KOBAYASHI M, DE LA CRUZ M, et al. Microsatellite markers in avocado (Persea americana Mill.): development of dinucleotide and trinucleotide markers [J]. Scientia Horticulturae, 2004, 101(3): 255−267. DOI: 10.1016/j.scienta.2003.11.008
[16] BORRONE J W, BROWN J S, TONDO C L, et al. An EST-SSR-based linkage map for Persea americana Mill. (avocado) [J]. Tree Genetics & Genomes, 2009, 5(4): 553−560.
[17] BORRONE J W, SCHNELL R J, VIOLI H A, et al. PRIMER NOTE: Seventy microsatellite markers from Persea americana Miller (avocado) expressed sequence tags [J]. Molecular Ecology Notes, 2006, 7(3): 439−444. DOI: 10.1111/j.1471-8286.2006.01611.x
[18] ASHWORTH V E T M. Microsatellite markers in avocado (Persea americana mill.): genealogical relationships among cultivated avocado genotypes [J]. Journal of Heredity, 2003, 94(5): 407−415. DOI: 10.1093/jhered/esg076
[19] LAVI U, HILLEL J, VAINSTEIN A, et al. Application of DNA fingerprints for identification and genetic analysis of avocado [J]. Journal of the American Society for Horticultural Science, 1991, 116(6): 1078−1081. DOI: 10.21273/JASHS.116.6.1078
[20] GROSS-GERMAN E, VIRUEL M A. Molecular characterization of avocado germplasm with a new set of SSR and EST-SSR markers: genetic diversity, population structure, and identification of race-specific markers in a group of cultivated genotypes [J]. Tree Genetics & Genomes, 2013, 9(2): 539−555.
[21] MHAMEED S, SHARON D, KAUFMAN D, et al. Genetic relationships within avocado (Persea americana Mill) cultivars and between Persea species [J]. Theoretical and Applied Genetics, 1997, 94(2): 279−286. DOI: 10.1007/s001220050411
[22] SHARON D, CREGAN P B, MHAMEED S, et al. An integrated genetic linkage map of avocado [J]. Theoretical and Applied Genetics, 1997, 95(5/6): 911−921.
[23] VIRUEL M A, GROSS E, BARCELO-MUNOZ A. Development of a linkage map with SSR and AFLP markers in avocado[A]. Proc. VI World Avocado Congress[C]//2007.
[24] RODRIGUEZ N N, FUENTES J L, COTO O, et al. Comparative study of polymorphism level, discrimination capacity and informativeness of AFLP, ISTR, SSR and Isoenzymes markers and agro-morphological traits in avocado[J]. Proc VI World Avocado Cogress, 2007. http://www.avocadosource.com/wac6/en/resumen/1c-43.pdf.
-
期刊类型引用(9)
1. 孙雨桐,刘德帅,冯美,齐迅,姚文孔. 果树分子标记辅助育种研究进展. 江苏农业学报. 2024(01): 183-192 .  百度学术
百度学术
2. 白玉娥,李今普,师鹏飞,王荣学,高颖,胡志健,杨荣. 基于表型性状的不同梨品种遗传多样性分析. 山东农业科学. 2024(02): 30-38 .  百度学术
百度学术
3. 刘东,孟瑾瑾,王盼,陈红刚,王惠珍,杜弢. 不同生态类型菘蓝SLAF-seq分子标记. 中草药. 2024(07): 2375-2382 .  百度学术
百度学术
4. 代建菊,李茂富,赵俊,慕尧,普天磊,袁建民,金杰. 云南不同栽培区域油梨果实品质差异分析. 西北植物学报. 2023(04): 656-666 .  百度学术
百度学术
5. 张雪芹,欧阳海波,谢志南,林丽霞,赖瑞云,钟赞华,林建忠. 不同品种油梨果实品质、光合特性比较及其相关分析. 南方农业学报. 2023(02): 405-413 .  百度学术
百度学术
6. 陈勇,李汶锺,彭林润,王明怀. 银木种子园及基于SNP标记的遗传分析. 湖南林业科技. 2023(03): 37-43 .  百度学术
百度学术
7. 李永涛,王振猛,杨庆山,周健,王莉莉,刘德玺,魏海霞. 山东省6个豆梨野生群体的遗传多样性分析. 中南林业科技大学学报. 2022(01): 138-145 .  百度学术
百度学术
8. 梁燕,韩传明,孙超,王翠香,闵旭峰,王静,王清海. 基于AFLP标记的薄壳山核桃种质资源遗传多样性分析. 江苏林业科技. 2022(01): 1-7 .  百度学术
百度学术
9. 郑斌,施晓龙,邹明宏. 基于枝条、叶和花的油梨种质表型多样性分析. 广东农业科学. 2020(09): 37-46 .  百度学术
百度学术
其他类型引用(4)




 下载:
下载: